Franklin by QIAGEN es una plataforma bioinformática en la nube diseñada para la gestión, análisis e interpretación de datos genómicos humanos. La solución centraliza la evaluación del caso, el control de calidad, la priorización de variantes y su clasificación en un flujo de trabajo estructurado, facilitando a los profesionales especializados la revisión e interpretación de datos complejos de secuenciación.
Descripción Detallada
Este software bioinformático en la nube ha sido desarrollado para el análisis de variantes germinales a partir de datos genómicos humanos procesados. Su enfoque integral permite trabajar con archivos FASTQ, BAM y VCF, aplicando pipelines bioinformáticos validados para alineamiento, llamada de variantes, anotación, interpretación y generación de informes personalizados.
Franklin integra en un único entorno la información genómica, fenotípica y técnica del caso, reuniendo metadatos clínicos, términos HPO, paneles, métricas de control de calidad y resultados del análisis. Esta visión unificada optimiza el flujo de trabajo y favorece una revisión más ágil, estructurada y consistente.
Además, su motor de priorización impulsado por inteligencia artificial selecciona las variantes con mayor probabilidad de relevancia para cada caso y las presenta en el Workbench para su revisión. Esta priorización incorpora clasificación automática según ACMG/AMP, correlación genotipo-fenotipo, modelos de herencia, segregación familiar y métricas técnicas asociadas a la confianza de la variante.
Para reforzar la interpretación, Franklin consolida evidencia procedente de más de 100 fuentes de información genética, génica y fenotípica, incluyendo bases de datos públicas, datos internos del laboratorio y curación comunitaria en tiempo real. De este modo, proporciona un entorno robusto para la evaluación de variantes y la estandarización de criterios de revisión.
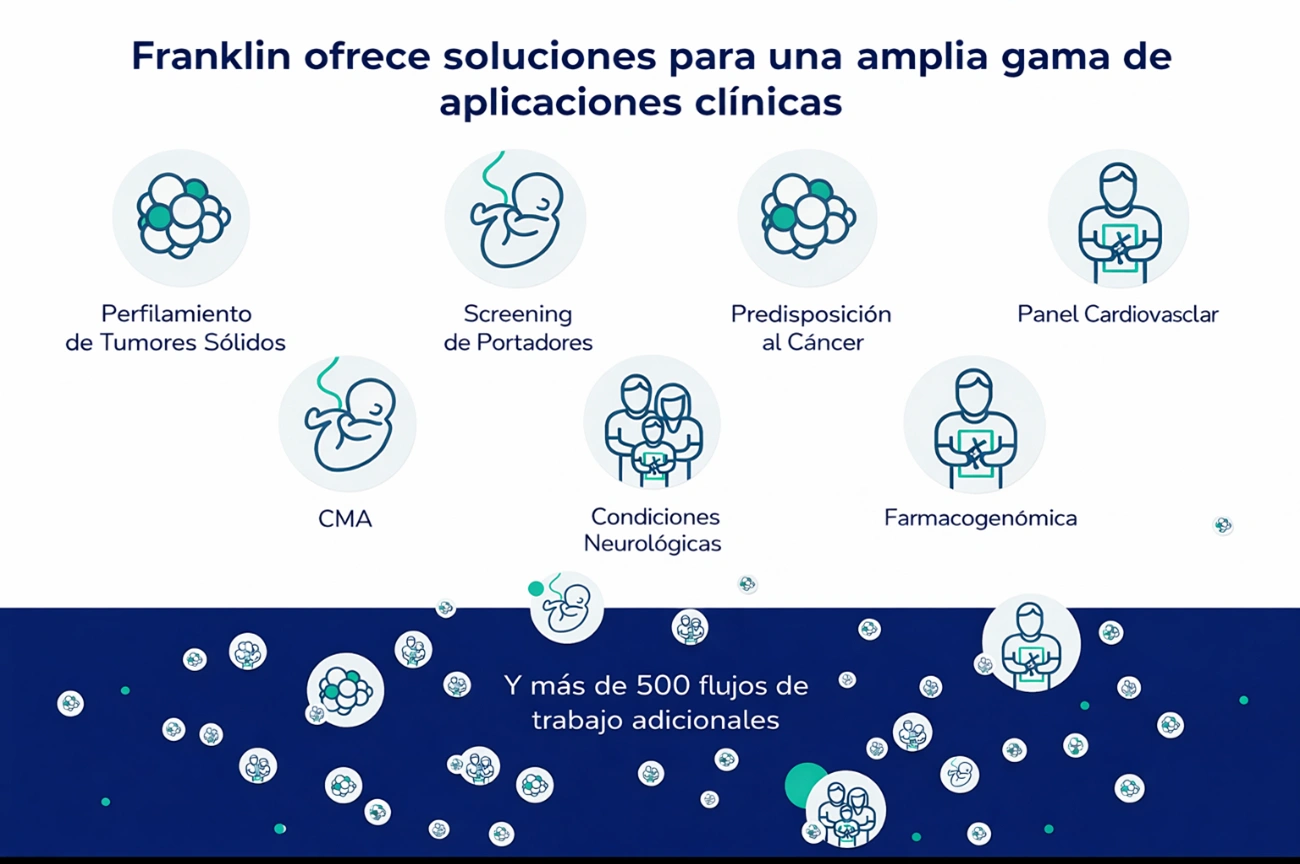
Aplicaciones clínicas
Beneficios
Público / Usuario previsto
Aspectos Clave


Área:
Tecnología:
Marca:
- Información básica sobre protección de datos
- Responsable: Diagnóstica Longwood S.L.
- Finalidad: Responder las consultas planteadas por el usuario y enviarle la información solicitada
- Legitimación: Consentimiento del usuario
- Destinatarios: Solo se realizan cesiones si existe una obligación legal.
- Derechos: Acceder, rectificar y suprimir, así como otros derechos, como se indica en la Política de Privacidad
Puede consultar la información completa en nuestra Política de Privacidad.
Productos relacionados

Sepsis Pathogenic Microorganism Detection Kit (Digital PCR)


VIASURE 16S V1-V4 NGS Solution

PN-900 CandidaGenius® C. auris screening assay

Illumina Viral Surveillance Panel v2